110年:(醫檢)檢驗(2)
下列那一個分型法之結果有資料庫可查詢且最易於分享與流通,可成為監控特定分型菌株是否在全球散佈?
A多位基因序列分型法( MLST )
B隨機複製多型性分型法( RAPD )
C重複序列聚合酶反應分型法( Rep-PCR )
D聚合酶反應結合單股結構多型性分析法( PCR-SSCP )
詳細解析
本題觀念:
本題考查的是**細菌分型方法(Bacterial Typing Methods)的特性比較,特別聚焦於「流行病學監測」、「資料庫共享」與「全球流通性」。核心觀念在於區分基於條帶(Band-based)與基於序列(Sequence-based)**的方法差異。
選項分析
-
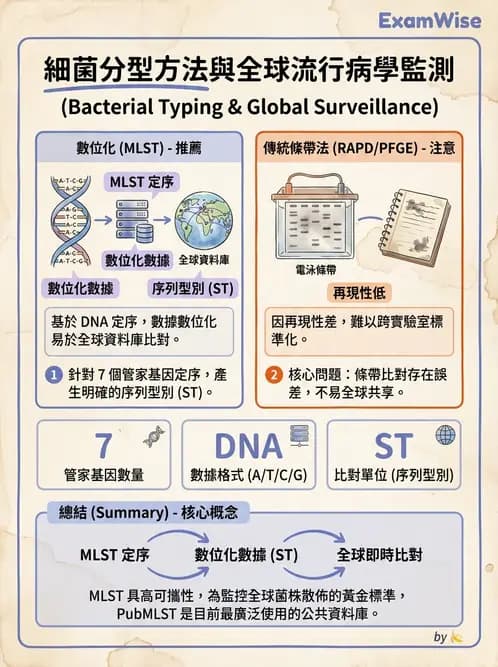
A. 多位基因序列分型法(Multilocus sequence typing, MLST):正確。
- 原理:針對細菌的 7 個(通常)管家基因(housekeeping genes)進行 PCR 擴增與定序。
- 資料庫與共享:因為結果是具體的「DNA 序列(A、T、C、G)」,數據是數位化且明確的(unambiguous)。這使得不同國家的實驗室可以將定序結果上傳至全球中心資料庫(如 PubMLST)進行比對,直接獲得序列型別(Sequence Type, ST)。
- 應用:由於其極高的再現性(reproducibility)與數據的可攜性(portability),MLST 是目前監控病原菌全球散佈(Global epidemiology)的黃金標準方法之一。
-
**B. 隨機複製多型性分型法(Random amplified polymorphic DNA,
...(解析預覽)...
升級 VIP 解鎖圖文解析