108年:(醫檢)檢驗(2)
下列何種方法可直接用於病理切片檢體中,檢測並觀察病原菌的存在?
A寡核酸陣列晶片( oligonucleotides array )
B原位螢光雜交法( fluorescence in situ hybridization, FISH )
C16S rRNA 定序
D16S -23S rRNA gene internal transcribed spacer (ITS )定序法
詳細解析
本題觀念:
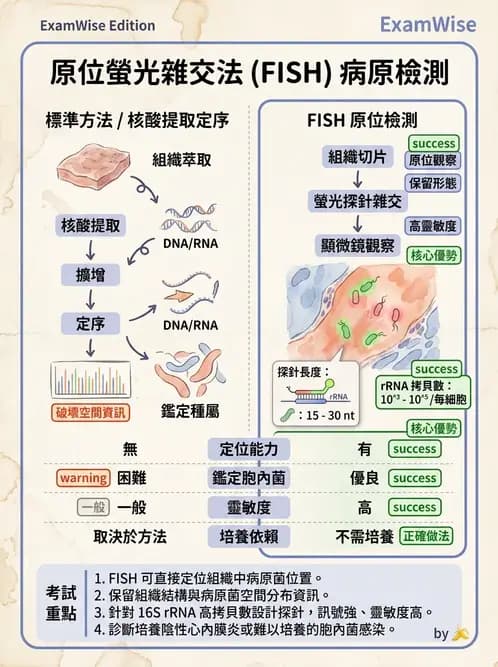
各種分子生物學方法在病理切片(pathology tissue section)檢體中的應用,尤其是哪種方法可以原位(in situ)直接在組織切片上觀察病原菌的存在與位置。
選項分析
(A) 寡核酸陣列晶片(oligonucleotides array) 錯誤。寡核酸微陣列晶片需要先從樣本中提取核酸,再進行擴增與標記,最後雜交到晶片上讀取訊號。這是提取後的體外分析,無法在組織切片原位觀察病原菌的空間位置。
(B) 原位螢光雜交法(fluorescence in situ hybridization, FISH) 正確,此為答案。 FISH 的核心特點是「原位(in situ)」——可直接在福馬林固定石蠟包埋(FFPE)切片或冰凍切片上,以螢光標記的 DNA/RNA 探針與目標序列(如細菌核糖體 RNA, rRNA)雜交,在螢光顯微鏡下直接觀察病原菌的存在位置,同時保留組織形態學資訊。適用範圍包括:血液培養陰性心內膜炎、胃腸道感染、分枝桿菌感染、胞內菌等。
(C) 16S rRNA 定序 錯誤。16S rRNA 定序需要先從樣本中提取細菌 DNA,經 PCR 擴增後定序比對,是識別細菌種屬的有力工具,但無法「直接在切片上觀察」病原菌的位置,破壞了組織空間資訊。
**(D)
...(解析預覽)...
升級 VIP 解鎖圖文解析