114年:(醫檢)檢驗(1)
下列何者方法最適合鑑定未知細菌抗藥性基因的變異?
A全轉錄組定序(whole transcriptome sequencing)
B全外顯子定序(whole exome sequencing)
C全基因組定序(whole genome sequencing)
D標的基因定序(targeted sequencing)
詳細解析
本題觀念
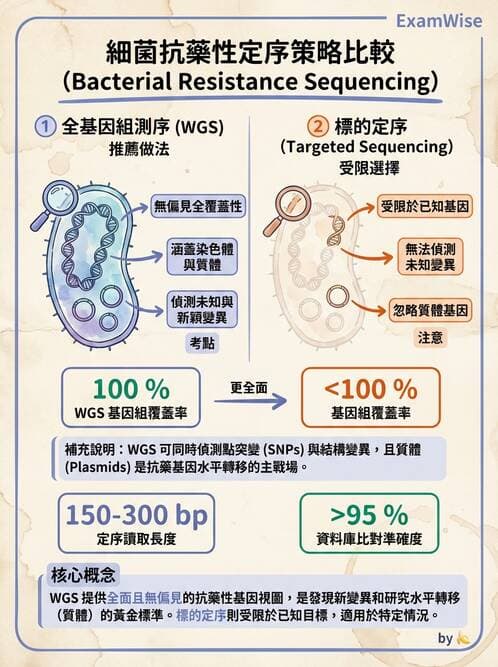
此題探討在細菌基因體中如何「無偏地」且「全面地」偵測未知抗藥性基因或其變異。重點在於選擇最適合用於新變異(novel variant)發現的高通量定序(NGS)策略。
選項分析
-
選項A:全轉錄組定序(whole transcriptome sequencing)
RNA-Seq 僅分析細胞中轉錄出的 RNA,著重基因表現量與轉錄本結構;若抗藥基因在特定條件下未被表現,或變異位於非轉錄區(例如調控序列、噬菌體插入元件),RNA-Seq 均無法涵蓋與偵測,故無法用於全面性的未知抗藥基因變異鑑定(en.wikipedia.org)。 -
選項B:全外顯子定序(whole exome sequencing)
Exome sequencing 專為區域捕獲人類外顯子而設計,細菌沒有典型的外顯子/內含子結構,且此方法僅選定「已知」編碼區域;無法偵測細菌基因組中非編碼區或新穎基因,與本題需求不符。 -
選項C:全基因組定序(whole genome sequencing)
WGS 以「無假設」方式讀取細菌整條染色體,能夠同時涵蓋所有編碼與非編碼區域,偵測已知與未知抗藥基因及其突變。不論是位於質體、染色體或移動遺傳
...(解析預覽)...
升級 VIP 解鎖圖文解析