113年:(醫檢)檢驗(1)
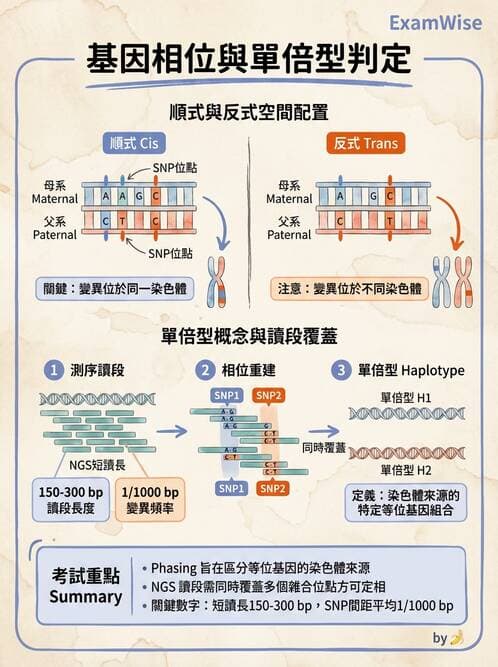
已知有兩個單一核苷酸多型性(single nucleotide polymorphism, SNP)位點相距約 5 個核苷酸,下列那個檢測技術,最能夠簡易分辨此兩個多型性位點位於同一條染色體(順式/cis)或不同條染色體(反式/trans)上?
Asingle-strain conformational polymorphism, SSCP
B次世代定序(next-generation sequencing, NGS)
C單一核苷酸多型性微陣列(SNP microarray)
D單一核苷酸延展反應 (single nucleotide extension, SNE)
詳細解析
本題觀念:
探討兩個相距極近(約5 nt)SNP定位於同一條染色體(cis)或不同染色體(trans),屬於「相位」(phasing)問題,關鍵在於檢測技術是否能在單一分子讀段內同時捕捉到兩位點的序列資訊。
選項分析
-
選項A SSCP(single-strand conformational polymorphism)
SSCP將PCR產物去雙股,藉單股DNA的3D折疊形態差異於凝膠中遷移速率不同來檢測是否存在序列變異,但不提供確切序列,也無法同時讀取兩個SNP的位點組合,自然無法判定SNP間相位(en.wikipedia.org)。 -
選項B 次世代定序(NGS)
NGS可產生100–300 bp(短讀)或更長(長讀)序列讀段,若兩SNP相距5 nt,幾乎必落在同一讀段內,直接觀察讀段上兩異位基因的配對組合,即可明確判別cis或trans;相關演算法(如SHAPEIT2的phase‐informative reads擴充版)專門利用此原理進行相位重建,能直接提供haplotype資訊([pubmed.ncbi.nlm.nih.gov](https://pubmed.ncbi.nlm.nih.go
...(解析預覽)...
升級 VIP 解鎖圖文解析