110年:(醫檢)檢驗(1)
關於桑格定序法( Sanger sequencing )分析的敘述,下列何者錯誤?
AG、A、 T、 C的訊號高度不適合作為核苷酸相對比例的標準
B檢測的變異位點愈靠近 sequencing primer 愈好
C應進行雙向( bidirectional )序列分析
D應先訂定訊號強度( peak intensity )、基線波動( baseline fluctuation )、訊號與雜訊比例( signal-to-noise ratio)等判讀標準
詳細解析
本題觀念:
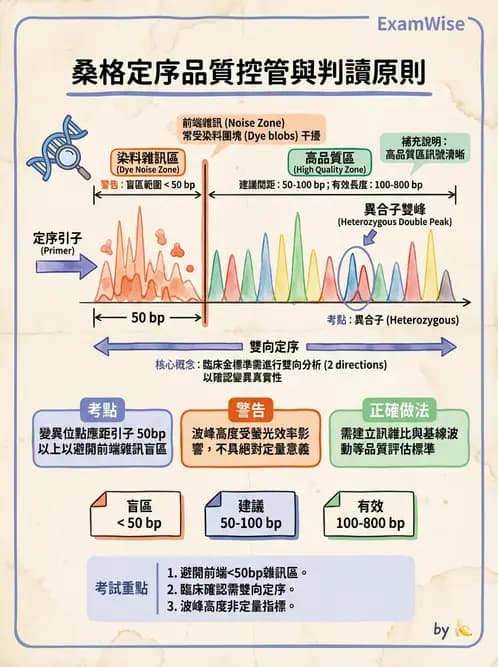
本題考查**桑格定序法(Sanger sequencing)的品質控制(Quality Control)與引子設計(Primer Design)**原則。核心概念在於了解定序反應的有效讀取範圍(Read length)、訊號特徵以及臨床判讀的標準作業程序。
選項分析
-
A. G、A、 T、 C的訊號高度不適合作為核苷酸相對比例的標準:正確
- 桑格定序使用四種不同的螢光染料標定 ddNTP。由於不同染料的量子產率(Quantum yield)與螢光強度不同,且 DNA 聚合酶對不同核苷酸的結合效率也會受到序列環境(Sequence context)影響,因此不同鹼基的波峰高度(Peak height)並不具有絕對的定量線性關係。
- 雖然在異合子(Heterozygote)檢測中,我們會觀察同一位置是否有高度減半的雙峰(Double peaks),但在不同位置或不同鹼基之間,訊號高度不能直接作為核苷酸濃度的絕對定量標準。
-
B. 檢測的變異位點愈靠近 sequencing primer 愈好:錯誤
- 這是本題的正確答案。
- 桑格定序在引子(Primer)之後的前 15~50 個鹼基(bases),常因未反應的染料團
...(解析預覽)...
升級 VIP 解鎖圖文解析