109年:(醫檢)檢驗(1)
在目前的次世代定序技術中,如果想針對大型基因中的點突變進行偵測,最理想的方式為:
A全基因體定序( whole genome sequencing )
B全外顯子定序( whole exome sequencing )
C目標區域定序( targeted sequencing )
D全轉 錄體定序( whole transcriptome sequencing )
詳細解析
本題觀念:
次世代定序(Next-Generation Sequencing, NGS)技術類型比較 — 針對大型基因點突變偵測的最佳策略
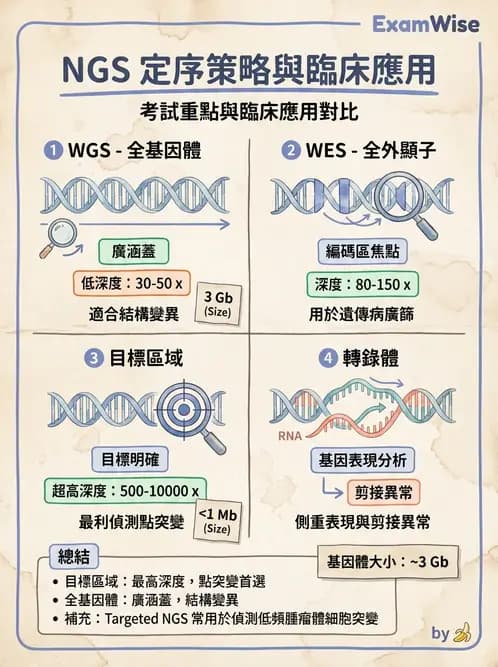
次世代定序(next-generation sequencing, NGS)技術依據涵蓋範圍與深度不同,分為四大類:全基因體定序、全外顯子定序、目標區域定序(targeted sequencing)、以及全轉錄體定序。在偵測**大型基因(large gene)的點突變(point mutation)**時,各技術有截然不同的效率與成本效益。
選項分析
(A) 全基因體定序(whole genome sequencing, WGS) WGS 涵蓋整個基因體(~3 × 10⁹ bp),可偵測所有突變類型,但若僅針對特定大型基因的點突變,WGS 的整體定序深度(depth/coverage)會被稀釋到很低(通常僅 30×),對低頻體細胞突變(low allele frequency)的靈敏度不足,且成本極高、分析時間長。不是「最理想」的選擇。
(B) 全外顯子定序(whole exome sequencing, WES) WES 針對所有蛋白質編碼外顯子(~1% 基因體,約 50–60 Mb),對點突變的涵蓋比 WGS 好,但若目標是單一大型基因,WES 仍需分攤定序深度到所有其他外顯子,效率不如針對性
...(解析預覽)...
升級 VIP 解鎖圖文解析