107年:(醫檢)檢驗(2)
下列何種方法常被用來檢測染色體 X-inactivation ?
ASouthern hybridization
BSNP array
CDNA sequencing
DMethylation-specific PCR
詳細解析
本題觀念:
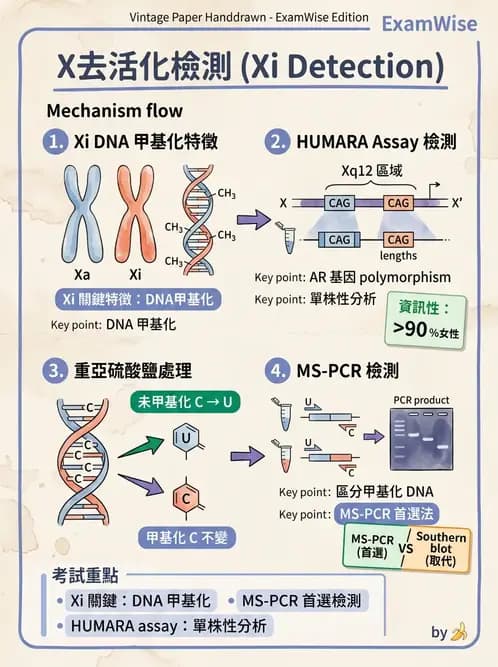
X 染色體去活化(X-inactivation)的偵測原理:利用 X 染色體去活化區域的 DNA 甲基化(methylation)差異來判斷哪一條 X 染色體被去活化。最常用的方法是甲基化特異性 PCR(methylation-specific PCR, MS-PCR),尤其是基於 HUMARA 基因的 HUMARA assay。
選項分析
(A) Southern hybridization Southern blot 雖然可以結合甲基化敏感性限制酶(如 HpaII)來分析 X 染色體去活化,且歷史上確實被使用,但它操作繁瑣、耗時、需要較多 DNA 量,現已逐漸被 PCR-based 方法取代,不是「常被用來」的現行主流方法。
(B) SNP array SNP array 可以廣泛偵測基因組的等位基因甲基化差異,但它的設計用途是基因組範圍的拷貝數變異(CNV)和多態性分析,並非針對性偵測 X 染色體去活化的常規工具。
(C) DNA sequencing DNA 定序可以分析序列變異,但單純的定序不能區分甲基化與未甲基化的 CpG 位點(需要搭配重亞硫酸鹽轉換 bisulfite sequencing 才能)。且本題問「常被用來」的方法,一般 DNA sequencing 不是 X-inactivation 的標準偵測
...(解析預覽)...
升級 VIP 解鎖圖文解析